-
印迹法和探针
-
印迹法是定性定量的
-
印迹法的关键是待测物的聚集和转移到膜上
-
探针
-
探针定义:用于指示(核酸,蛋白质,细胞结构的)标记分子,探针可以是DNA、RNA、有机小分子和金属离子。
-
核酸探针是使用放射性核素、生物素或者荧光物质等标记的核苷酸片段
-
原理:与待测片段以碱基互补配对原理杂交
-
-
-
印迹法分为DNA、RNA、蛋白质印迹法三大类(谁blotting就是谁在膜上跑)
-
DNA印迹法southern blotting用于DNA定性定量分析
- 需要限制性核酸内切酶消化
-
RNA印迹法northern blotting用于基因转录水平分析
-
不需要限制性核酸内切酶切割(因为RNA小,且变形RNA转移效率高)
-
缺点:检测敏感性比PCR低
-
优点:特异性强,假阳性率低,是最可靠的RNA定量方法之一
-
-
蛋白质印迹法western blotting=免疫印迹法,用于蛋白质表达和相互作用研究
- 用于检测特异性蛋白质存在、细胞中特异蛋白质半定量分析、蛋白质分子的互作
-
新方法
-
斑点印迹法=斑点杂交=点渍法
-
原位杂交ISH,结合荧光技术叫荧光原位杂交FISH
-
DNA-蛋白质印迹法southwestern blotting
-
RNA-蛋白质印迹法northwestern blotting
-
蛋白质-蛋白质印迹法farwestern blotting
-
生物芯片(与高通量芯片技术结合)
-
-
-
生物芯片:印迹法的微型化和集成化
-
基因芯片:差异表达分析
-
书上分法
-
测DNA:大规模检测和全基因组分析
-
测RNA:基因差异表达情况,mRNA逆转录出DNA回到上一条进行基因分析
-
-
导图分法
-
表达谱芯片
-
ChIP-chip
-
-
-
蛋白质芯片:分析蛋白质的表达水平和相互作用
-
基本原理:亲和反应
-
如抗原-抗体、受体-配体
-
已广泛应用于:蛋白质表达谱、蛋白质功能、蛋白质间相互作用、疾病诊断和药物筛选
-
缺点:不能像基因芯片那样覆盖整个基因组所表达的蛋白质
-
-
细胞、组织、类器官芯片
-
-
-
PCR
-
原理:体外DNA复制
-
反应体系:模板、耐热的TaqDNA聚合酶、引物、底物dNTP、缓冲体系
-
反应循环:变性、退火、延伸
-
-
应用:DNA扩增、放大检测、测序、突变等。地位:最基本的技术;高敏感、高特异、高产率、可重复、快速简便;分子生物学与医学研究的支撑技术
-
简便快速的获得大量目的基因片段
-
定性定量分析微量DNA和RNA
-
简化了DNA序列分析
- 实现高通量DNA测序分析的基础
-
提高基因突变检测的敏感性
-
和其他技术结合
-
单链构象多态性分析
-
等位基因特异的寡核苷酸探针分析
-
基因芯片技术
-
DNA序列分析
-
-
-
-
PCR衍生技术广泛应用
-
逆转录PCR=RT-PCR:获得目的基因和定性与半定量分析RNA
- 最有效、最广泛
-
原位PCR=in situ PCR:扩增与定位目的基因
-
弥补了PCR技术和原位杂交技术的不足
-
重大实用价值
-
-
实时PCR=real-time (fluorescence)PCR=实时荧光PCR=定量聚合酶链反应=qPCR
-
定量的关键是每一轮测一次PCR产物量:利用荧光信号积累,建立实时扩增曲线
-
实时荧光分为两大类
-
非引物探针类
-
(周围环境放置)荧光染料SYBR Green 结合新合成的DNA
-
成本低廉、简单易行、应用广泛
-
-
引物探针类
-
(直接荧光标记)仅在靶序列杂交或引导扩增时产生荧光:特异性更高,结合彩色探针可多基因同时检测
-
TaqMan探针法
-
分子信标(molecular beacon)
-
荧光共振能量转移FRET探针法(fluorescence resonance energy transfer)
-
-
-
应用场景:有定量、特异、灵敏、快速的特点,应用广泛
-
肿瘤:测基因变化(DNA分析)和表达量(肿瘤RNA逆转录为DNA分析)
-
基因多态性分析:SNP分析(单核苷酸多态性分析)→个体精准用药
-
病原体检测:灵敏度高、取样少、快速简便
-
-
-
-
-
DNA测序
-
经典方法
-
桑格-库森法=双脱氧法=链终止法(均匀的在每一个A处停止合成,得到长度不同的片段,跑一下)
-
化学降解法=DNA化学测序法=碱基特异性裂解法(比如固定在A断,得到长度不同的片段,跑一下)
-
-
高通量测序HTS(high-throughput sequencing):基于桑格测序法
-
自动激光荧光DNA测序
-
自动激光荧光DNA测序仪(第一代测序)
- 链终止法加四色荧光法
-
Illumina测序平台(第二代测序)

-
-
焦磷酸测序
- 焦磷酸测序=454测序(第二代测序)
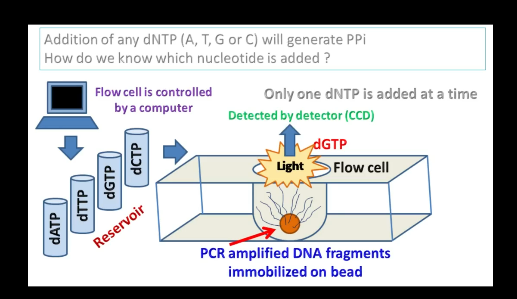
- 离子半导体测序
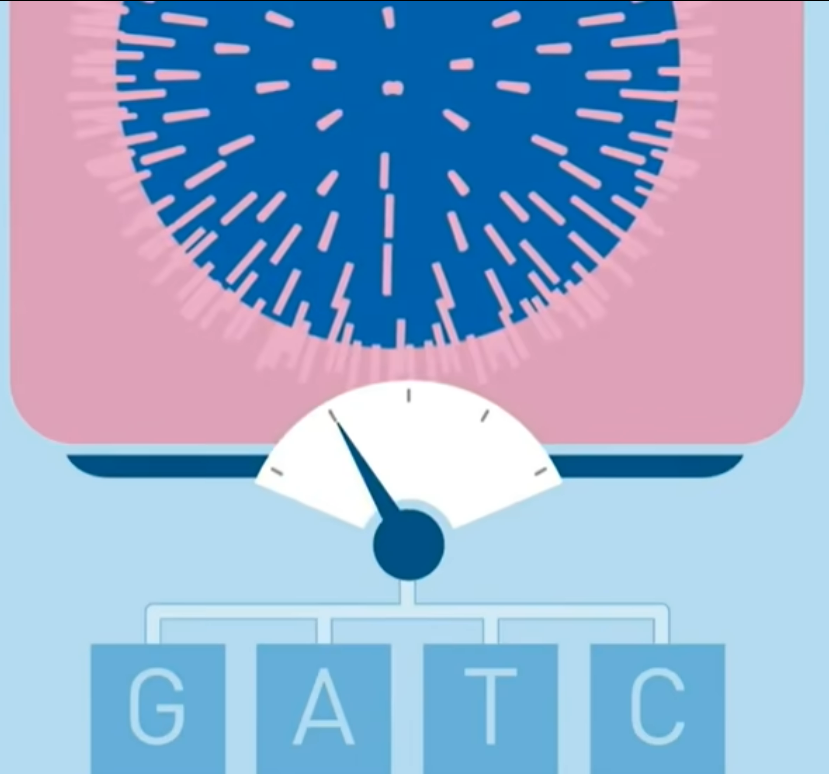
- 焦磷酸测序=454测序(第二代测序)
-
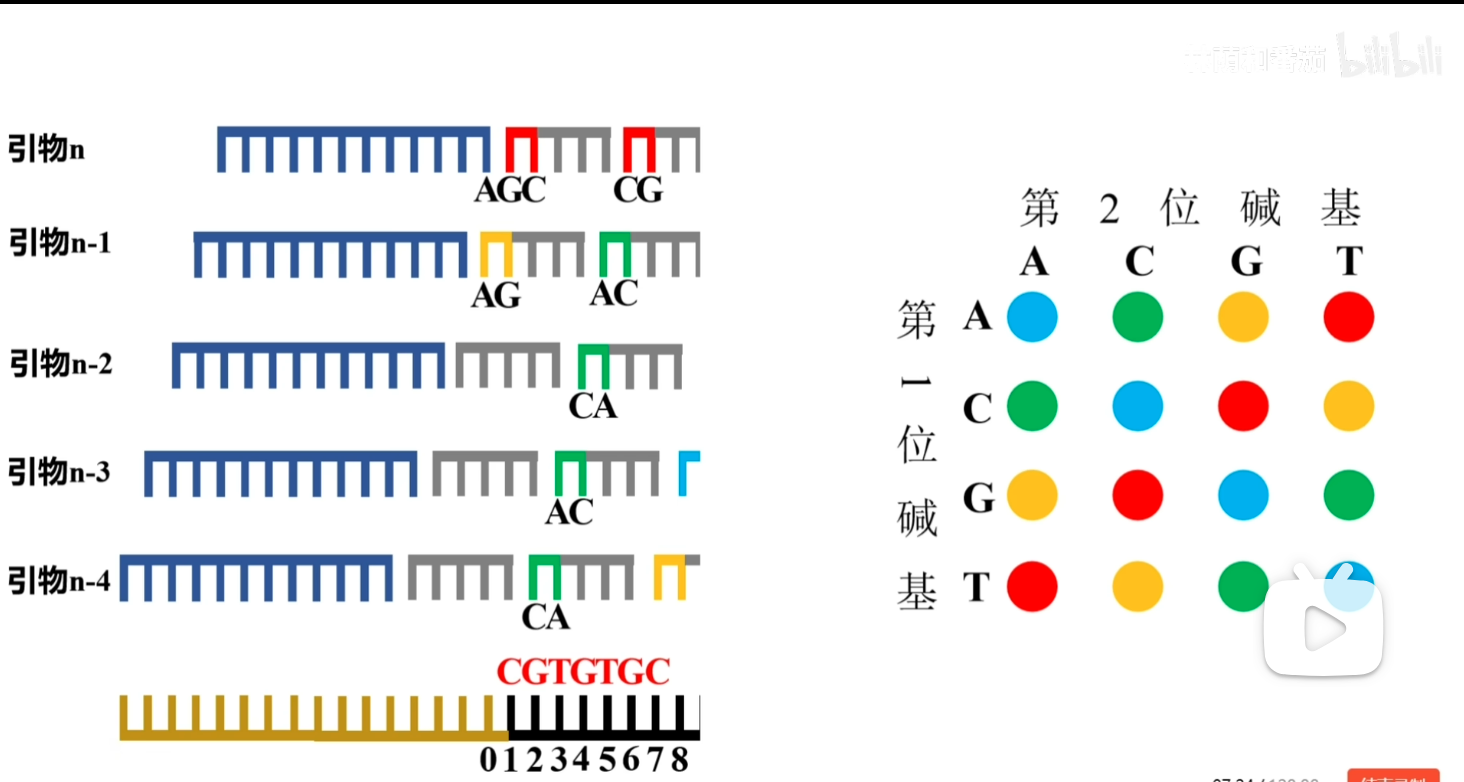
SOLiD测序(第二代测序):用DNA连接酶代替DNA聚合酶
-
(DNA)单分子测序(第三代测序):已成为空间组学和时空组学的的主要技术
-
HeliScope单分子测序

-
SMRT测序=单分子实时测序(single molecule real time sequencing)

-
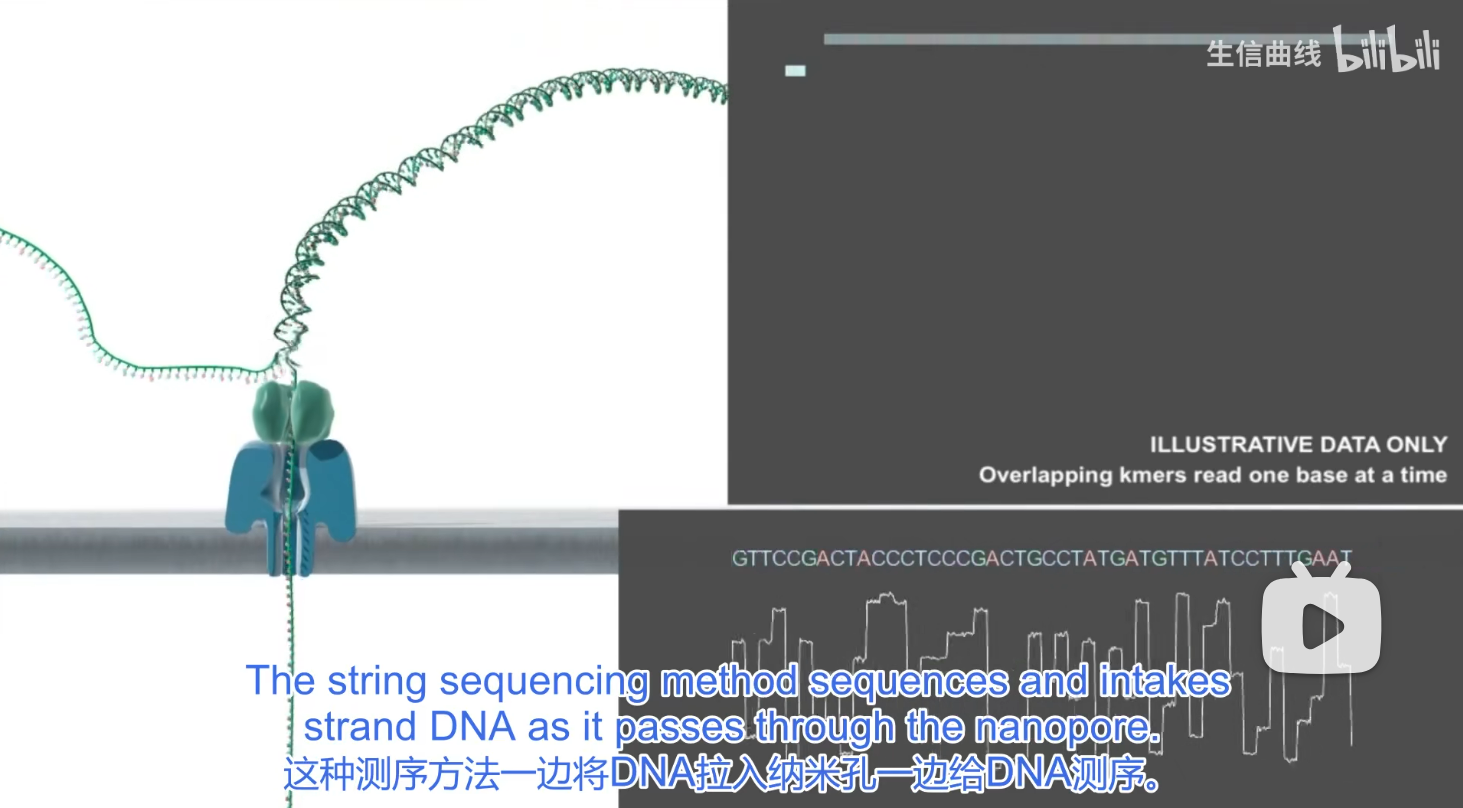
纳米孔测序
-
-
-
应用:基因变异、药物敏感性、外源微生物、法医个体鉴别
-
高通量促进了以下测序进步
-
全基因组测序(whole genome sequencing ,WGS)
-
转录物组测序(transcriptome sequencing)=RNA测序(RNA-seq)
-
外显子组测序(exome sequencing)
-
染色质免疫共沉淀测序(ChIP-seq)
-
-
主要用途:
-
人群大样本分析
-
肿瘤
-
个人基因组分析
-
病原微生物检测
-
其他:亲子鉴定
-
-
-
-
生物大分子互作
-
导论分类
-
体外:测定生物分子相互作用速率、亲和力
-
等温滴定量热(isothermal titration calorimetry,ITC)
-
表面等离子共振( surface plasmonresonance,SPR)
-
生物膜层干涉( bio-layer interferometry,BLI)
-
微量热泳动(microscale thermophoresis,MST)
-
表面增强拉曼光谱(surface-enhanced Raman spectroscopy,SERS)技术
-
-
体内外互作
-
各种亲和分离分析(如亲和色谱、免疫共沉淀、标签蛋白质沉淀和串联亲和纯化等)
-
酵母双杂交系统(yeast two-hybrid system)
-
FRET效应分析
-
噬菌体展示(phage display)系统
-
细胞指数富集配体系统进化( cell systematic evolution of ligand by exponential enrichment,cell-SELEX)
-
-
分子互作
-
核磁共振
-
晶体衍射
-
冷冻电镜
-
分子计算
-
-
-
蛋白质互作技术:解析功能机制
-
标签蛋白质牵拉沉淀实验:标签加已知蛋白作为钓饵
-
GST融合蛋白质牵拉沉淀实验GST pull-down assay
-
使用的酶:谷胱甘肽S转移酶GST
-
结合后洗脱琼脂糖珠使用:还原型谷胱甘肽洗脱液GSH
-
-
(镍离子六组氨酸标签):镍离子琼脂糖珠结合的6个连续组氨酸(6xHis)标签
-
-
双酵母杂交
-
原理
-
和上游启动子结合的酵母转录激活因子GAL4分为BD和AD,BDAD结合在一起结合在启动子才能使转录启动
-
bait诱饵:BD-x(就是BD结合已知蛋白)
-
pray猎物:AD-x(就是AB结合未知蛋白)
-
两者一结合,就能启动转录
-
反之启动转录说明已知蛋白和未知蛋白结合
-
-
应用
-
已知基因序列的蛋白质互作
-
已知存在互作则用于找功能结构域或关键氨基酸残基
-
待研究蛋白质做成诱饵,用可能结合的蛋白回推到cDNA库,确定能和待研究蛋白结合的蛋白质
-
-
-
-
核酸蛋白质互作技术:解析基因表达调控机制
-
因为核酸蛋白质互作为非共价可逆结合,作用力弱,所以有以下两种不同实现方法
-
使用温和生理条件
-
甲醛、紫外光交联(固定)
-
-
电泳迁移率变动分析(EMSA)=凝胶阻滞分析=凝胶移位结合分析=DNA结合分析:通过分子量变化确定,结合后分子量变大,条带滞后(温和)
-
用于研究DNA结合蛋白质和相应DNA序列的互作
-
也可应用于蛋白质-DNA、蛋白质RNA的相互作用研究
-
(非变性聚丙烯凝胶酰胺电泳:不加SDS十二烷基磺酸钠,以免造成复合物解离)
-
-
染色质免疫沉淀技术ChIP:探究真核生物表达机制(体内)
-
地位:目前研究体内DNA与蛋白质互作的主要方法(固定)
-
联用:能在全基因组范围内高通量筛选细胞或组织中蛋白质和核酸的相互作用,检测蛋白质结合位点,基因位点特异性组蛋白修饰模式和位置
-
ChIP和芯片技术联用→基于微阵列(芯片)的染色质免疫沉淀(ChIP-chip)
-
ChIP和测序技术联用→染色质免疫沉淀测序
-
-
-
-
-
基因表达分析
-
生信挖掘数据库信息是第一步(基因数据库)
-
特定基因表达分析
-
查询:同源检索,使用局部序列比对检索基本工具BLAST(basic local alignment search tool):追踪不同细胞组织或状态下该基因表达的信息
-
实验研究该基因在设定条件下基因表达情况和功能分析,进一步注释该基因
-
-
直接间接分析某个生物个体细胞或组织等基因表达谱及其各自丰度
-
查询
-
生信工具挖掘
-
有,实验验证
-
没有,用基因表达综合数据库GEO(gene expression omnibus data base)推荐的技术开展实验研究,再展开生信分析 其表达模式
-
-
-
-
染色质构象捕获技术可以解析基因表达时空特异性的机制(空间数据库)
-
线性染色质易受表观遗传改变即染色质重塑(chromatin remodeling)改变了染色质可及性(chromatin accessibility),所以要检测染色质构象
-
染色质构象捕获3C(chromatin conformation capture)
-
基于3C扩展的技术可以从单个位点构象捕获到全基因组远程互作
-
环状染色质构象捕获技术4C(circular 3C, 4C)
-
染色质构象捕获碳拷贝技术5C(3C carbon copy)
-
高通量染色质构象捕获技术Hi-C(high-throughout 3C)
-
-
与免疫共沉淀(ChIA-PET)、核酸杂交、单细胞、高通量测序技术和生信偶联,促进了时空特异性的表达
-
-
鉴定基因功能区域可以了解基因表达及其调控(拷贝数分析)
-
导论
-
明确转录区(了解表达的基础)
-
鉴定顺式作用元件和探测基因空间位置(了解表达的关键)
-
分析表达产物(了解表达的时空特性)
-
比较基因表达差异(机体感知态势和应对的分子过程)
-
-
确定基因编码区(cDNA文库和RNA剪接分析):得到编码序列
-
cDNA文库
-
保守序列合成
-
分析产物观察拼接方式
-
设计核酸探针
-
-
cDNA末端快速扩增法RACE(rapid amplification of cDNA end)
-
5'-RACE(打碎加上基因特异性引物,就是每个基因不同,每个引物cDNA复合物不同)
-
3'-RACE(通用多聚A尾扩增)
-
已知序列在中间,靠3'近的未知序列扩增叫3'-RACE,靠5'近的未知序列扩增叫5'-RACE。
-
-
RNA剪接分析
-
DNA芯片分析
-
交联免疫沉淀法
-
体外报告基因=报道基因:就是表达荧光的基因
-
常用的报告基因有
-
荧光素酶基因
-
绿色荧光蛋白基因
-
β-葡萄糖苷酶基因
-
-
-
-
-
确定转录起点TSS(transcription start site)(直接克隆测序和5'-RACE)(这块以下为真核)
-
逆转录合成全长cDNA(直接克隆然后测序,结尾片段就是转录起点)
-
5'-RACE
-
SAGE规模化地检测基因表达种类及其丰度
-
SAGE=基因序列表达系列分析=serial analysis of gene expression:在5'末端引入特殊的Ⅱ型限制性核酸内切酶位点,把所有短片段当成标签串联在一起,这样既能获得种类,又能获得相对含量
-
CAGE=帽分析基因表达=cap analysis gene expression
-
-
-
确定启动子(启动子克隆和核酸-蛋白质互作)
-
PCR结合测序技术分析启动子
-
核酸-蛋白质互作分析启动子
-
EMSA和ChIP确定基因序列中含有反式作用因子的结合位点
-
酶足迹法
-
化学足迹法
-
DNA测序
-
-
-
-
-
基因表达产物和时空特异性检测是基因表达分析的核心内容(定位分析)
-
拷贝数分析技术可以了解基因表达丰度
-
分子标记了解基因表达的组织和细胞内定位
-
酶联免疫吸附实验分析蛋白质
- 酶联免疫分析ELISA(enzyme linked immunosorbent assay)
-
免疫组化实验原位检测组织或细胞表达的蛋白质
-
免疫组织化学
-
免疫细胞化学
-
常用技术有
-
酶免疫组化(酶标记)
-
免疫荧光组化(荧光标记,可用荧光或激光共聚焦显微镜观察)
-
免疫金组化(胶体金标记)
-
-
-
流式细胞术:分析表达特异蛋白质的阳性细胞
-
-
-
整体基因表达谱信息可以通过转录物组学分析技术获得(转录物组学)
-
导论
-
转录物组学(tanscriptomics)是通过分析细胞内全部 RNA转录产物,研究细胞中所有基因转录及转录调控规律的学科领域。
-
RNA-seq、生物芯片、SAGE、大规模平行标签测序(massively parallel signature sequencing.MPSS)等高通量技术分析转录物,可以获得基因表达谱,即基因在不同细胞或组织、不同时间或发育阶段的总体表达水平,进而生物信息学分析并展示差异表达基因,从而推断基因间的表达调控和表达产物间的相互作用,揭示基因与疾病发生、发展的内在关系。
-
-
比较组学:获得动态可变的差异表达基因
-
MPSS
-
消减杂交( subtractive hybridizaion)=扣除杂交:扣除相似表达从而获得差异表达基因
- 差示筛选、消减探针、消减文库的建立
-
mRNA差异显示(mRNA differential display,mRNA-DD )=差异显示逆转录 PCR(differential display reverse transcriptin PCR,DDRT-PCR ):分析不同状态细胞cDNA
-
-
空间组学:获得全局性的基因表达时空特异性
-
-
全面蛋白质表达修饰和互作谱信息可以通过蛋白质组学技术获得(蛋白质组学)
-
导论
-
蛋白质组(proteome)是指细胞、组织或机体在特定时间和空间上表达的所有蛋白质。
-
蛋白质组学(proteomics)=全景式蛋白质表达谱(globalprotein expressionprafile)分析:蛋白质组研究对象,分析细胞内动态变化的蛋白质组成、定位、结构、表达式及功能模式的学科领域,包括鉴定蛋白质的表达、存在方式(修饰形式)或部位、结构、功能和相互作用等
-
组学信息分析
-
实验分析
- 高通量鉴定蛋白质组主要是通过生物芯片、二维电泳、二维/多维液相分离等,然后质谱法(massspectrometry,MS)鉴定。
-
-
质谱法可以高通量鉴定蛋白质种类和一级结构信息
-
肽质量指纹图PMF
-
串联质谱法tandem mass spectrometry
-
-
各种修饰:质谱法
-
蛋白质种类和结构鉴定是蛋白质组研究的基础
- 二维电泳和多维色谱并结合生物质谱法、蛋白质印迹法、蛋白质芯片等技术,对蛋白质进行全面的种类和结构鉴定研究
-
翻译后修饰的鉴定有助于蛋白质功能的阐明
- 质谱法、抗体技术、蛋白质组学技术和基因编辑技术等多种技术的应用,已能够深入探査蛋白质修饰的类型、位置和功能
-
-
蛋白质互作研究:认识蛋白质功能的重要内容
-
酵母双杂交
-
各类亲和层析
-
荧光共振能量转移
-
-
-
生化第十八章常用分子生物技术梳理
发布于 2025-08-24 432 次阅读


Comments NOTHING